# Librerías
library(readxl) # Para leer los excels
library(dplyr) # Para tratamiento de dataframes
library(ggplot2) # Nice plots
library(caret) # For data paratition
library(MASS) # funciones lda() y qda()
library(klaR) # partimatAnálisis Discriminante: salud
Introducción
En este notebook se va a explicar el método de Análisis de Discriminante Lineal y Cuadrático con el objetivo de clasificar una variable binaria. Mediante un ejemplo práctico se mostrará como llevar a cabo dichas técnicas.
dataset
En este cuaderno vamos a analizar el dataset llamado salud.xlsx. Este contiene microdatos relativos a la Encuesta Nacional de Salud. Concretamente, datos correspondientes al año 2017. Las variables de interés son las siguientes:
- EDAD: Identificación del adulto seleccionado: Edad.
- SEXO: Identificación del adulto seleccionado: Sexo.
- Altura: Altura en cm.
- Peso: Peso en kg.
El objetivo de este estudio será aplicar un Análisis Discriminante para intentar clasificar el sexo de la población a partir del resto de variables.
Descripción del trabajo a realizar
Se pretende hacer un Análisis de Discriminante empleando los procedimientos de LDA (Análisis de Discriminante Lineal) y QDA (Análisis de Discriminante Cuadrático).
- Hacer un análisis exploratorio. Ver si las variables separan bien las clases.
- Convertir a factor la variable respuesta.
- Realizar una partición de datos Train/Test.
- Fijar semilla cuando se usen números aleatorios (para la reproductividad).
- Ejecutar algoritmos lda/qda y evaluar su bondad.
Análisis Exploratorio (EDA)
EDA viene del Inglés Exploratory Data Analysis y son los pasos relativos en los que se exploran las variables para tener una idea de que forma toma el dataset.
Cargar Librerías
Lo primero de todo vamos a cargar las librerías necesarias para ejecutar el resto del código del trabajo:
Lectura datos
Ahora cargamos los datos del excel correspondientes a la pestaña “Datos” y vemos si hay algún NA o algún valor igual a 0 en nuestro dataset. Vemos que no han ningún NA (missing value) en el dataset luego no será necesario realizar ninguna técnica para imputar los missing values o borrar observaciones.
Cargamos entonces el conjunto de datos:
datos <- read_excel("../../../../files/salud.xlsx", sheet = "Datos")Veamos un resumen de los datos y si hay algún NA para quitarlo/imputarlo.
datos$Edad <- as.numeric(datos$Edad)
datos$Altura <- as.numeric(datos$Altura)
datos$Peso <- as.numeric(datos$Peso)
summary(datos) Edad Sexo Altura Peso
Min. : 15.00 Length:23089 Min. :120.0 Min. : 26.00
1st Qu.: 39.00 Class :character 1st Qu.:160.0 1st Qu.: 62.00
Median : 52.00 Mode :character Median :166.0 Median : 71.00
Mean : 52.84 Mean :166.7 Mean : 72.66
3rd Qu.: 67.00 3rd Qu.:173.0 3rd Qu.: 81.00
Max. :103.00 Max. :204.0 Max. :180.00
NA's :1070 NA's :1070 NA's :1070 cat("Hay un número de NA's igual a: ",sum(is.na(datos)),"\n")Hay un número de NA's igual a: 4280 Análisis de Discrminante: LDA y QDA
Introducción
El análisis discriminante es una técnica estadística utilizada para clasificar observaciones en grupos o categorías predefinidas en función de un conjunto de variables predictoras.
El objetivo principal es identificar las características o variables que mejor distinguen entre diferentes grupos conocidos. Es una técnica de aprendizaje supervisado, lo que significa que requiere un conjunto de datos etiquetado con información sobre las categorías o grupos a los que pertenecen las observaciones.
El análisis discriminante se puede dividir en dos tipos principales:
Análisis Discriminante Lineal (LDA): LDA asume que las variables predictoras tienen una distribución normal y que las matrices de covarianza de las variables predictoras son iguales para todos los grupos. LDA busca un hiperplano (o límite de decisión) que maximice la distancia entre las medias de los grupos y minimice la varianza dentro de cada grupo. Debido a la asunción de igual covarianzas, los hiperplanos que separan las clases son lineales.
Análisis Discriminante Cuadrático (QDA): QDA relaja la suposición de igualdad de matrices de covarianza y permite que cada grupo tenga su propia matriz de covarianza. Esto hace que QDA sea más flexible pero también requiere más datos para estimar las matrices de covarianza para cada grupo. Los hiperplanos que separan las clases son cuadráticos.
Ahora grafiquemos los histogramas de las variables distinguiendo entre variable respuesta a ver si alguno de ellos parece separar bien las variables y por tanto es susceptible de que funcione luego bien en LDA/QDA.
Vamos a dibujar las densidades de las variables distinguiendo entre las clases de la variable respuesta para ver si alguna de las variables permite una clara separación entre variables.
library(ggplot2)
ggplot(datos, aes(Edad)) +
geom_density(aes(group = Sexo, colour = Sexo, fill = Sexo), alpha = 0.1) +
theme(text = element_text(size = 9))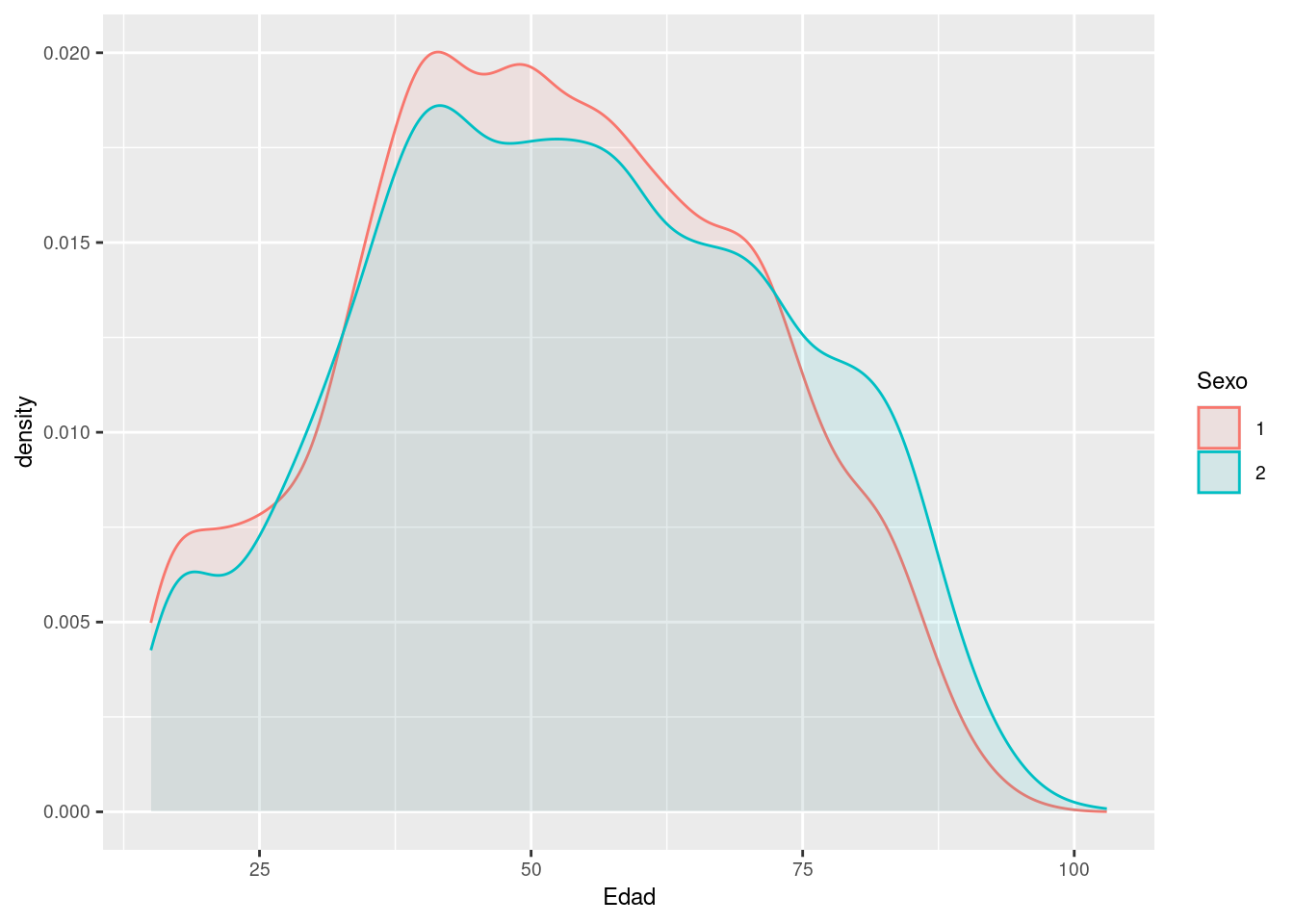
library(ggplot2)
ggplot(datos, aes(Altura)) +
geom_density(aes(group = Sexo, colour = Sexo, fill = Sexo), alpha = 0.1) +
theme(text = element_text(size = 9))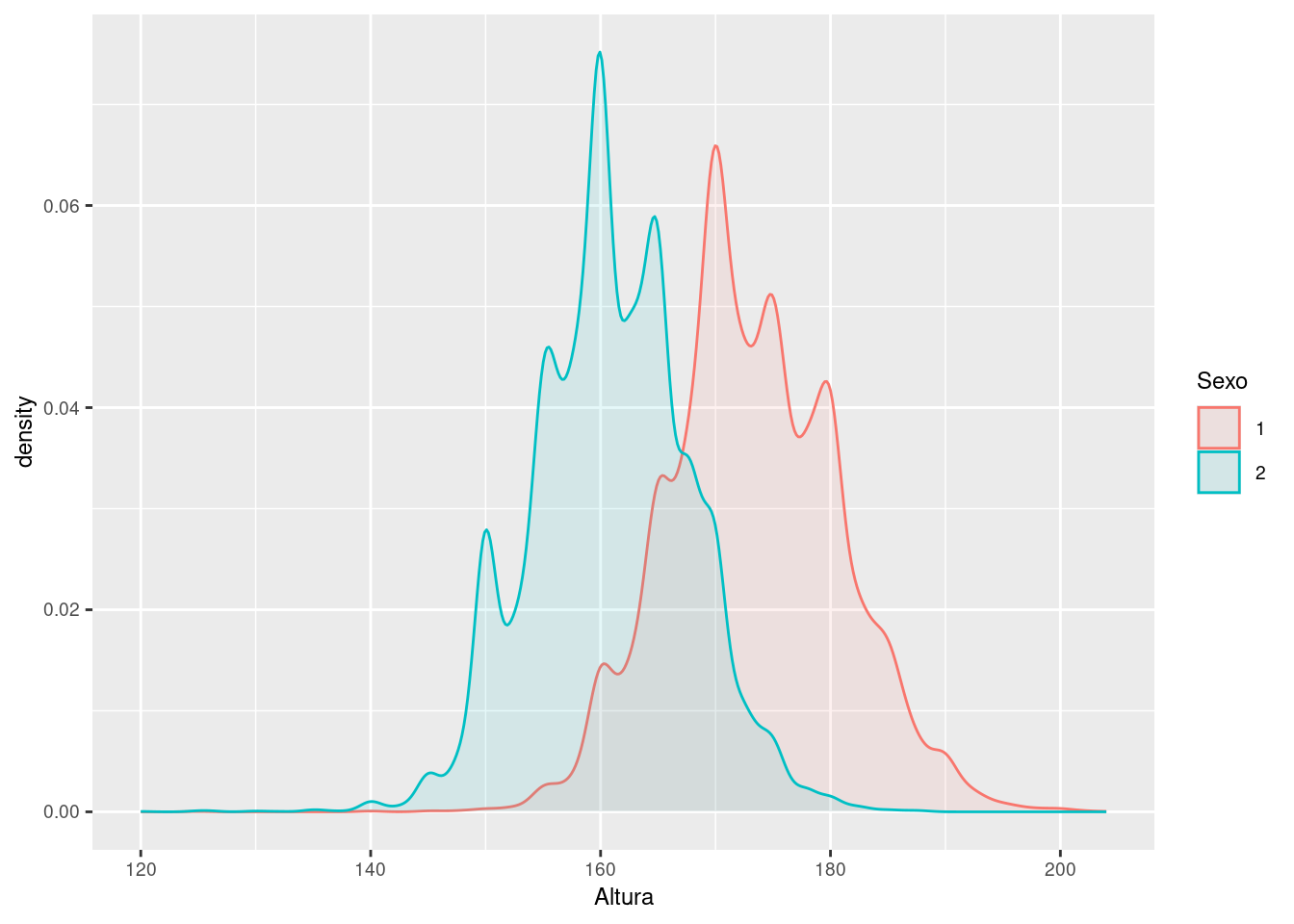
library(ggplot2)
ggplot(datos, aes(Peso)) +
geom_density(aes(group = Sexo, colour = Sexo, fill = Sexo), alpha = 0.1) +
theme(text = element_text(size = 9))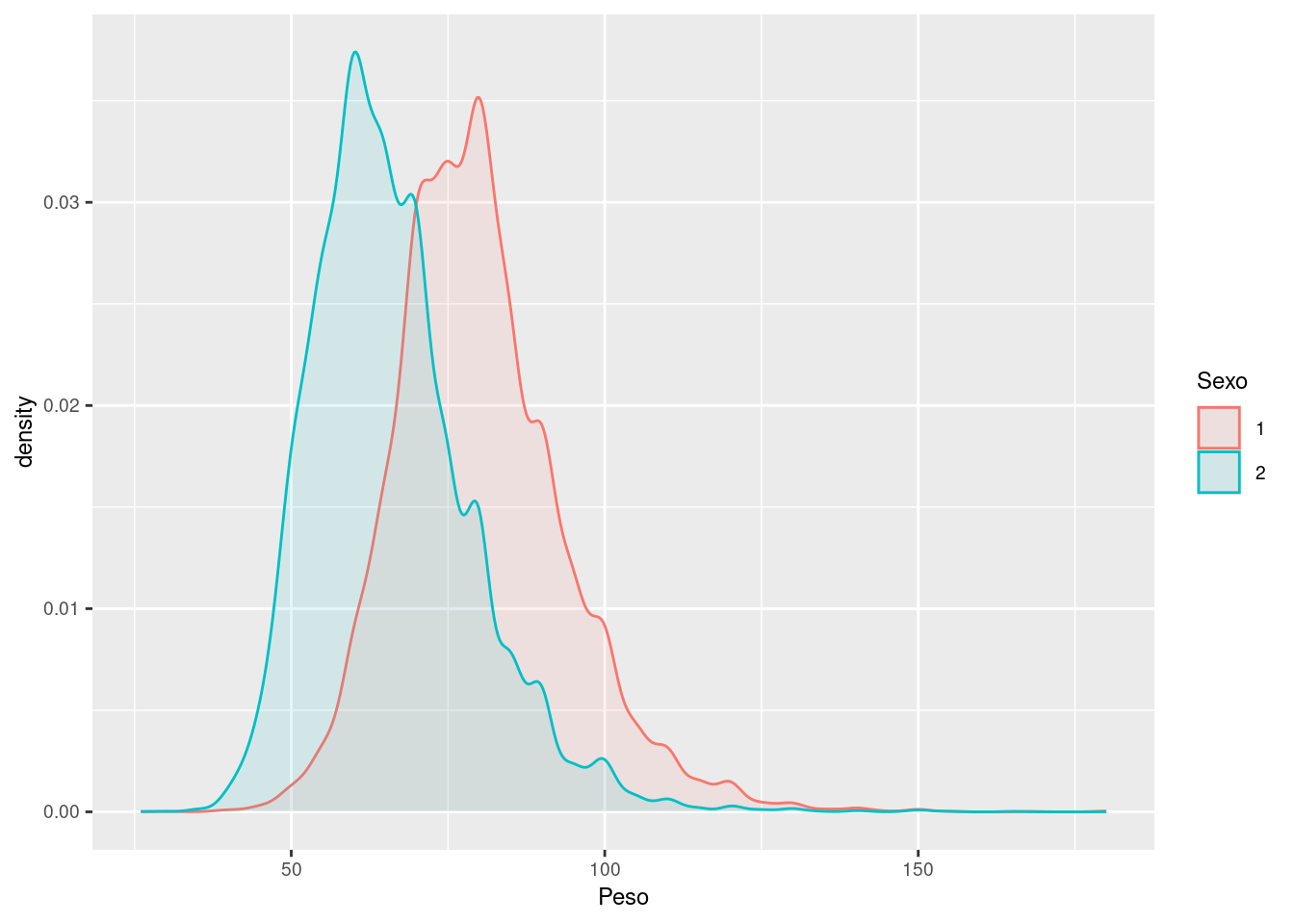
Como cabía esperar, la variable edad no discrimina bien el sexo de una persona debido a que no hay una relación directa. Sin embargo, tanto en las variables peso como altura se observa como la clase 1 (hombres) muestran valores más altos que las mujeres en ambas variables. Esto puede ser un buen indicador a la hora de discriminar.
Veamos ahora en 2D las clasificaciones y observamos que hay buenas discriminaciones, luego todo nos hace pensar que los métodos de después funcionarán bastante bien.
datos$Sexo <- as.factor(datos$Sexo)
Label <- datos$Sexo
colo <- c("pink", "#1874CD")[Label]
X <- datos[, c(1, 3:4)]
pairs(X, main = "Diabetes data set", pch = 20, col = colo, lower.panel = NULL, cex = 0.2, oma = c(1, 3, 3, 15))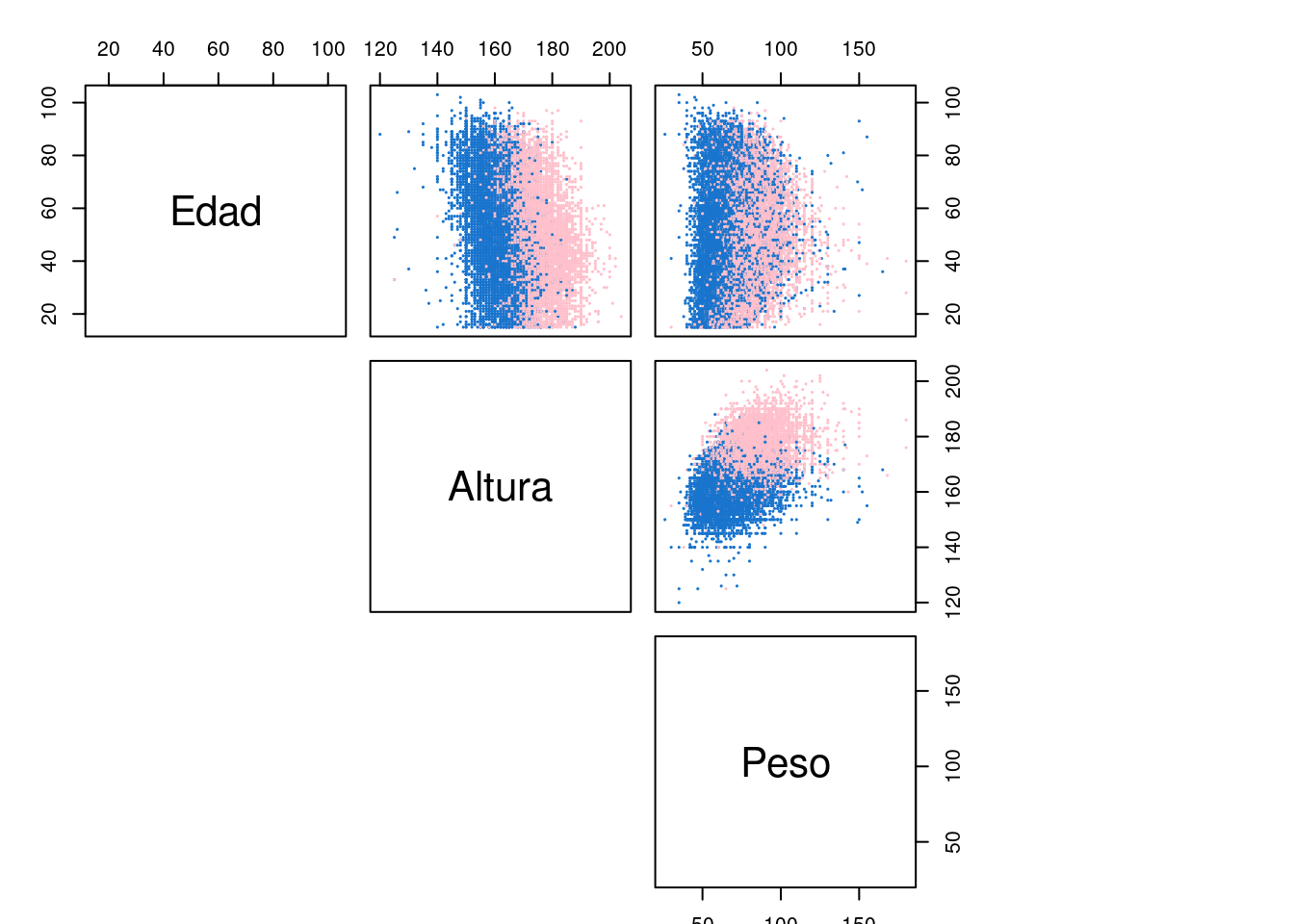
MUY IMPORTANTE CONVERTIR LA VARIABLE RESPUESTA A FACTOR ya que representa dos clases, es decir, es una variable cualitativa.
datos$Sexo <- as.factor(datos$Sexo)Partición de datos
Para evitar el overffiting debido a que el modelo se ha entrenado demasiado con los datos proporcionados, vamos a realizar una partición de datos y una vez entrenado el modelo, lo evaluaremos con la partición segunda.
Para ello usamos la función caret::createDataPartition() que nos permite mantener la proporción de la variable binaria respuesta. En caso de no usar esta función podríamos estar dejando en la partición de entreno observaciones con la misma variable respuesta y dejar la clase minoritaria infrarepresentada, lo que podría incurrir en un mal ajuste del modelo para dicha clase.
set.seed(785248) # For Reproducibility
spl <- createDataPartition(datos$Sexo, p = 0.75, list = FALSE) # 75% for training
saludTrain <- datos[spl, ]
saludTest <- datos[-spl, ]Análisis de Discriminante Lineal (LDA)
Como se ha comentado previamente:
- Se supone que la distribución de los datos es una normal multivariante.
- Supone que todas las matrices de covarianzas son iguales ( y por tanto el clasificador es lineal).
set.seed(785248) # For Reproducibility
lda.class.salud <- lda(Sexo ~ Altura + Peso + Edad, data = saludTrain)
# qda.class.diabetes
plot <- partimat(Sexo ~ Altura + Peso + Edad, data = saludTrain, method = "lda")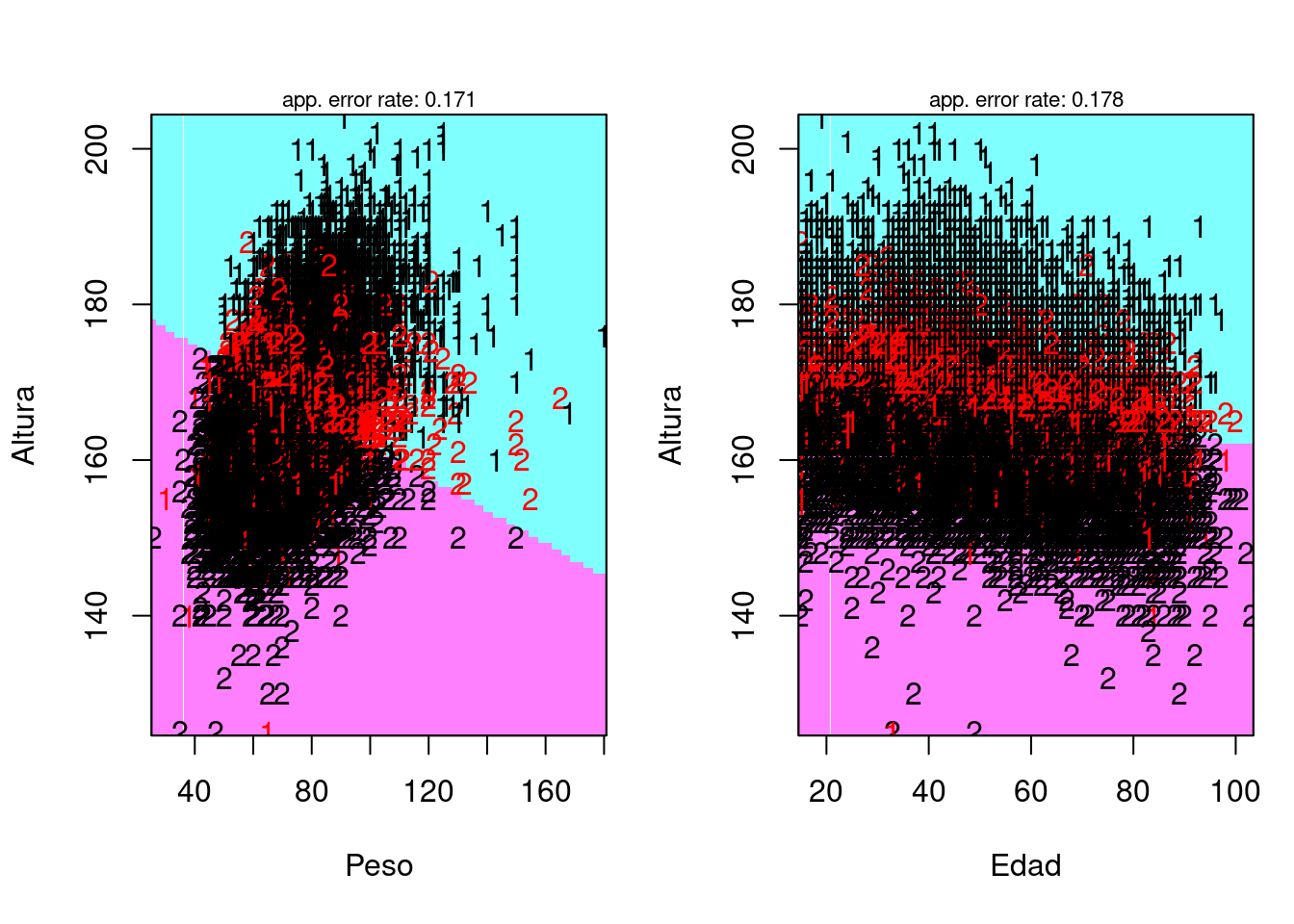
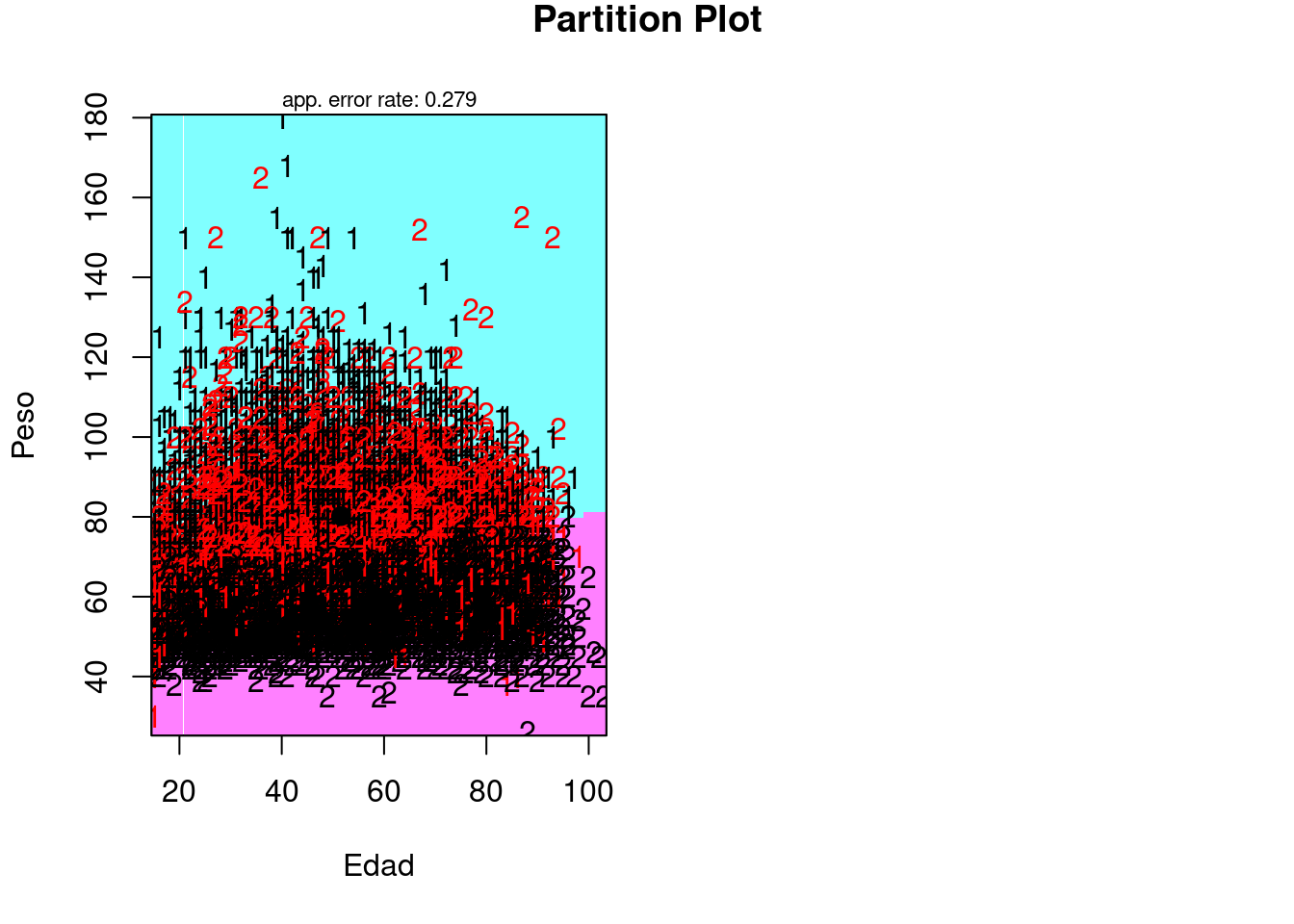
set.seed(785248)
# predict with the lda model and test data
pred.lda <- predict(lda.class.salud, saludTest)$class
# confusion matrix
confusionMatrix(pred.lda, saludTest$Sexo)Confusion Matrix and Statistics
Reference
Prediction 1 2
1 2072 411
2 507 2514
Accuracy : 0.8332
95% CI : (0.8231, 0.843)
No Information Rate : 0.5314
P-Value [Acc > NIR] : < 2.2e-16
Kappa : 0.6644
Mcnemar's Test P-Value : 0.001716
Sensitivity : 0.8034
Specificity : 0.8595
Pos Pred Value : 0.8345
Neg Pred Value : 0.8322
Prevalence : 0.4686
Detection Rate : 0.3765
Detection Prevalence : 0.4511
Balanced Accuracy : 0.8314
'Positive' Class : 1
Exactitud (Accuracy): La exactitud del modelo es del 83%, lo que significa que el modelo clasificó correctamente aproximadamente el 83% de las instancias en el conjunto de prueba.
Sensibilidad (Sensitivity o Recall): La sensibilidad del modelo para la clase 1 es del 80%, lo que indica que el modelo identificó correctamente alrededor del 80% de las instancias de la clase 1 en el conjunto de prueba.
Especificidad (Specificity): La especificidad del modelo para la clase 0 es del 85%, lo que significa que el modelo identificó correctamente alrededor del 85% de las instancias de la clase 0 en el conjunto de prueba.
En general, estos resultados muestran que el modelo LDA tiene un rendimiento bueno en la clasificación de las instancias en el conjunto de prueba, con una exactitud y un kappa significativos.
Análisis de Discriminante Cuadrático
Como se ha comentado previamente:
- Se supone que la distribución de los datos es una normal multivariante.
- NO supone que todas las matrices de covarianzas son iguales ( y por tanto el clasificador es cuadrático y no lineal).
- Método muy inestable a menos que tengamos muestras muy grandes y de dimensiones bajas.
Es más inestable debido a que al permitir que cada grupo tenga su propia matriz de covarianza, aunque lo que lo hace más flexible, requiere muchos más datos para estimar las matrices de covarianza para cada grupo.
set.seed(785248) # For Reproducibility
qda.class.salud <- qda(Sexo ~ Altura + Peso + Edad, data = saludTrain)
# qda.class.diabetes
plot <- partimat(Sexo ~ Altura + Peso + Edad, data = saludTrain, method = "qda")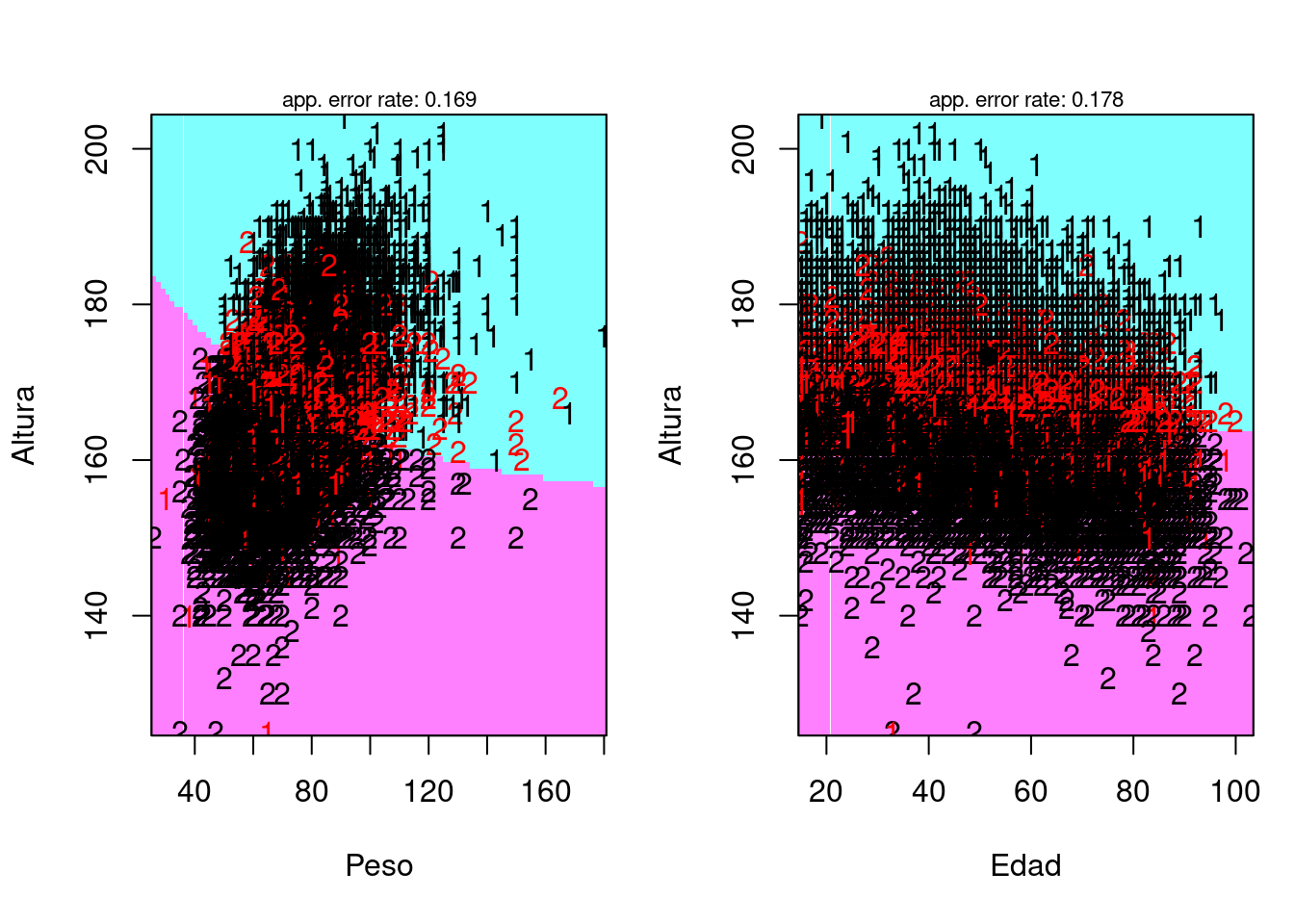
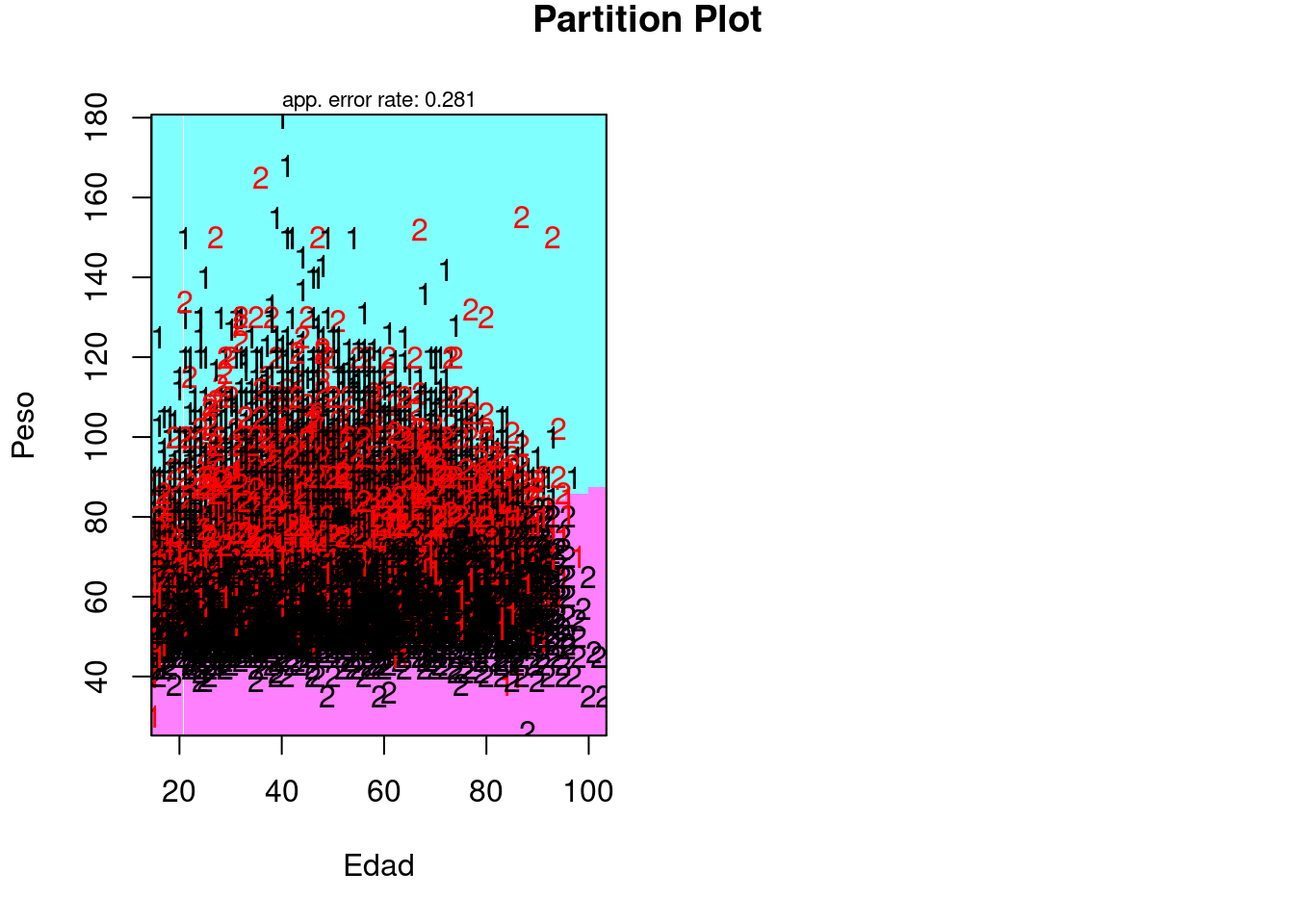
set.seed(785248)
# predict with the lda model and test data
pred.qda <- predict(qda.class.salud, saludTest)$class
# confusion matrix
confusionMatrix(pred.qda, saludTest$Sexo)Confusion Matrix and Statistics
Reference
Prediction 1 2
1 2068 412
2 511 2513
Accuracy : 0.8323
95% CI : (0.8222, 0.8421)
No Information Rate : 0.5314
P-Value [Acc > NIR] : < 2.2e-16
Kappa : 0.6625
Mcnemar's Test P-Value : 0.001257
Sensitivity : 0.8019
Specificity : 0.8591
Pos Pred Value : 0.8339
Neg Pred Value : 0.8310
Prevalence : 0.4686
Detection Rate : 0.3757
Detection Prevalence : 0.4506
Balanced Accuracy : 0.8305
'Positive' Class : 1
Exactitud (Accuracy): La exactitud del modelo es del 83%, lo que significa que el modelo clasificó correctamente aproximadamente el 83% de las instancias en el conjunto de prueba.
Sensibilidad (Sensitivity o Recall): La sensibilidad del modelo para la clase 1 es del 80%, lo que indica que el modelo identificó correctamente alrededor del 80% de las instancias de la clase 1 en el conjunto de prueba.
Especificidad (Specificity): La especificidad del modelo para la clase 0 es del 85%, lo que significa que el modelo identificó correctamente alrededor del 85% de las instancias de la clase 0 en el conjunto de prueba.
Comparando estos resultados con los del modelo LDA, observamos ambos modelos tienen una exactitud, sensibilidad y valor predictivo negativo parecidos.
Conclusión
En el presente estudio se ha visto como poder clasificar el Sexo de individuos en sus respectivas clases, de acuerdo a variables de edad, altura y peso. Se ha certificado que esto es posible y que la variable Edad no tiene sentido incluirla ya que en función de la Edad de una persona no es posible clasificar su sexo.Estos hechos han permitido discriminar bastante bien la variable respuesta mediante modelos de Análisis de Discriminante Lineal y Cuadrático.
